ゼロがなくなったポアソン分布のパラメーターをData augmentationで推定する [統計]
ゼロがなくなったポアソン分布のパラメーターをData augmentation(データ拡大)で推定するということをやってみたメモです。
【追記 2017-12-09 10:30】 すみません。Nの計算を間違えていました(松浦さん、ご指摘ありがとうございます)。ということで、修正しました。
元データを生成します。
library(rstan) set.seed(123) N <- 100 lambda <- 2 ## Original data x1 <- rpois(N, lambda) ggplot(data.frame(x = x1)) + geom_bar(aes(x))
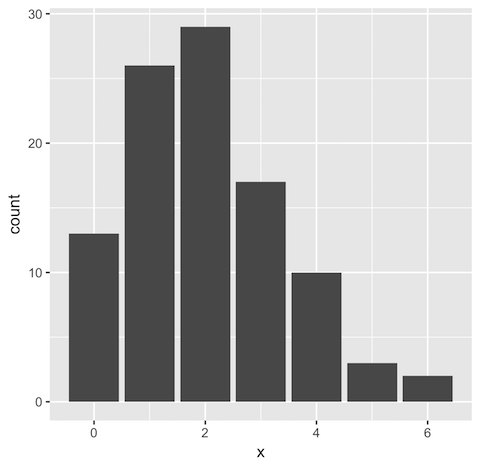
> mean(x1) [1] 2.02
ゼロの部分を消去して切断データにします。
## Truncated data x2 <- x1[x1 > 0] ggplot(data.frame(x = x2)) + geom_bar(aes(x)) + xlim(0, NA)
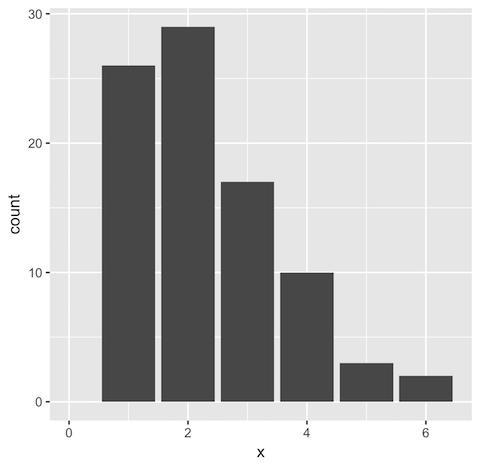
> length(x2) [1] 87 > mean(x2) [1] 2.321839
ダミーデータを加えます(Data augmentation)。
## Data Augmentation x3 <- c(x2, rep(0, 400))
元データ(切断前のデータ)が拡大後のデータにしめる割合です。
> N / length(x3) [1] 0.2053388
Stanのプログラムです。Zero-Infrated modelと同型です。omegaは、元データ(切断前のデータ)が拡大後のデータにしめる割合です。【修正】前のコードではomegaの範囲を[C/M, 1]としていましたが、Nの計算方法を修正したので、ここも[0, 1]としました。
data {
int<lower = 0> M;
int<lower = 0> X[M];
}
transformed data {
int C = 0; // Number of non-zero data
for (m in 1:M)
C = C + ((X[m] > 0) ? 1 : 0);
}
parameters {
real<lower = 0> lambda;
real<lower = 0, upper = 1> omega;
}
model {
for (m in 1:M) {
if (X[m] > 0) {
1 ~ bernoulli(omega);
X[m] ~ poisson(lambda);
} else {
target += log_sum_exp(bernoulli_lpmf(0 | omega),
bernoulli_lpmf(1 | omega)
+ poisson_lpmf(0 | lambda));
}
}
}
generated quantities {
int<lower = C, upper = M> N;
{
// Bern(1 | ω) Pois(0 | λ) /
// (Bern(1 | ω) Pois(0 | λ) + Bern(0 | ω))
real p = (omega * exp(-lambda))
/ (omega * exp(-lambda) + (1 - omega));
N = C + binomial_rng(M - C, p);
}
}
【修正】前のコードではp = omega - real_C / M;としていましたが、上のように修正しました。
RStanから実行しました。
fit <- stan("DA.stan",
data = list(M = length(x3), X = x3))
結果です。
Inference for Stan model: DA.
4 chains, each with iter=2000; warmup=1000; thin=1;
post-warmup draws per chain=1000, total post-warmup draws=4000.
mean se_mean sd 2.5% 25% 50% 75% 97.5% n_eff Rhat
lambda 2.02 0.00 0.17 1.70 1.91 2.02 2.14 2.37 2503 1
omega 0.21 0.00 0.02 0.17 0.19 0.21 0.22 0.25 2432 1
N 100.86 0.09 4.69 93.00 98.00 100.00 104.00 111.00 2976 1
lp__ -252.00 0.02 0.98 -254.61 -252.37 -251.69 -251.29 -251.03 1639 1





コメント 0