『ポアソン分布・ポアソン回帰・ポアソン過程』をRで再現してみる(7) [統計]
点配置の比較をしてみます。Stanをつかいます。
まずは比較対象の点配置を生成します。図5.2(b)の非定常ポアソン過程と同様のものとします。
### 5.6
## Stanによるパラメーター推定
library(ggplot2)
library(dplyr)
## データを生成
set.seed(1)
r <- function(x, y) {
(-0.00002 * (x - 40)^2 + 0.05) * 0.04 * y
}
x.min <- 0
x.max <- 100
y.min <- 0
y.max <- 100
opt <- optim(par = c(1, 1),
fn = function(par) -r(par[1], par[2]),
method = "L-BFGS-B",
lower = c(x.min, y.min),
upper = c(x.max, y.max))
r.S <- -opt$value
N <- rpois(1, r.S * (x.max - x.min) * (y.max - y.min))
## 非定常ポアソン過程で点を生成
df <- data.frame(x = runif(N, x.min, x.max),
y = runif(N, y.min, y.max),
r = runif(N, 0, 1)) %>%
filter(r(x, y) / r.S > r) %>%
select(x, y)
ggplot(data = df, mapping = aes(x = x, y = y)) +
geom_point() +
xlim(x.min, x.max) +
ylim(y.min, y.max) +
coord_equal() +
theme(aspect.ratio = 1)
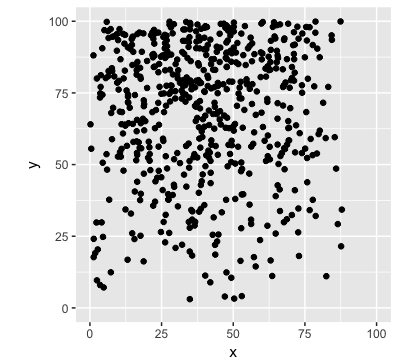
こまかく分割した領域を生成します。
n <- c(100, 100)
lx <- (x.max - x.min) / n[1]
ly <- (y.max - y.min) / n[2]
w <- expand.grid(x = seq(x.min + lx / 2, x.max - lx / 2, lx),
y = seq(y.min + ly / 2, y.max - ly / 2, ly))
比較する点配置を生成します。こちらは定常ポアソン過程とします。
## 定常ポアソン過程で点を生成 set.seed(2) np <- rpois(1, nrow(df)) px <- runif(np, x.min, x.max) py <- runif(np, y.min, y.max) df2 <- data.frame(x = px, y = py) ggplot(data = df2, mapping = aes(x = x, y = y)) + geom_point() + xlim(x.min, x.max) + ylim(y.min, y.max) + coord_equal() + theme(aspect.ratio = 1)
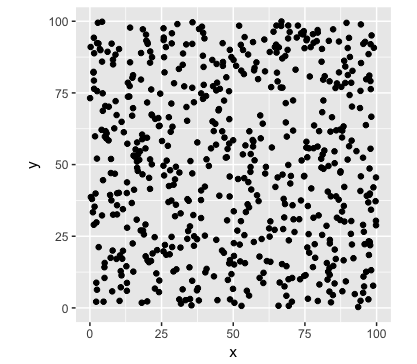
配置を比較します。推定するのはa0とa1というパラメーターで、a1>0ならば配置はかさなり、a1<0ならばたがいに背反の傾向にあるということになります。Stanコードは本の数式をだいたいそのままうつしてあります(というつもりです)。
Stanコード(ipp.stan)
functions {
real f(vector p, real sigma) {
real ret = exp(-(p[1]^2 + p[2]^2) / (2 * pi() * sigma^2))
/ (2 * pi() * sigma^2);
return ret;
}
vector k(matrix x, matrix p, matrix u, real sigma) {
vector[dims(x)[1]] s;
vector[dims(x)[1]] fout;
for (j in 1:dims(x)[1]) {
s[j] = 0;
for (i in 1:dims(p)[1])
s[j] = s[j] + f(x[j]' - p[i]', sigma);
fout[j] = 0;
for (i in 1:dims(u)[1])
fout[j] = fout[j] + f(u[i]' - x[j]', sigma);
}
return s ./ fout;
}
}
data {
int<lower = 0> NX;
int<lower = 0> NP;
int<lower = 0> NU;
matrix[NX, 2] X;
matrix[NP, 2] P;
matrix[NU, 2] U;
real<lower = 0> E;
real<lower = 0> sigma;
}
transformed data {
vector[NU] kU = k(U, P, U, sigma);
vector[NX] kX = k(X, P, U, sigma);
}
parameters {
real a0;
real a1;
}
model {
target += -sum(exp(a0 + a1 * kU) * E) + sum(a0 + a1 * kX);
}
Rコードです。
## RStan
library(rstan)
rstan_options(auto_write = TRUE)
options(mc.cores = parallel::detectCores())
fit2 <- stan("ipp.stan",
data = list(NX = nrow(df2),
NP = nrow(df),
NU = nrow(w),
X = as.matrix(df2),
P = as.matrix(df),
U = as.matrix(w),
E = lx * ly,
sigma = 2),
iter = 2000, warmup = 1000, thin = 1)
print(fit2)
結果です。a1はだいたい0に近い値となりました。
Inference for Stan model: ipp.
4 chains, each with iter=2000; warmup=1000; thin=1;
post-warmup draws per chain=1000, total post-warmup draws=4000.
mean se_mean sd 2.5% 25% 50% 75% 97.5% n_eff
a0 -2.85 0.00 0.06 -2.98 -2.89 -2.85 -2.81 -2.74 1391
a1 0.10 0.02 0.71 -1.31 -0.38 0.10 0.58 1.48 1414
lp__ -2235.28 0.03 1.02 -2238.08 -2235.69 -2234.95 -2234.56 -2234.30 1422
Rhat
a0 1
a1 1
lp__ 1
つぎに、同じ非定常ポアソン過程で生成させた配置と比較してみます。
## 同じ非定常ポアソン過程で点を生成
set.seed(3)
N <- rpois(1, r.S * (x.max - x.min) * (y.max - y.min))
df3 <- data.frame(x = runif(N, x.min, x.max),
y = runif(N, y.min, y.max),
r = runif(N, 0, 1)) %>%
filter(r(x, y) / r.S > r) %>%
select(x, y)
data.frame(df3) %>%
ggplot(mapping = aes(x = x, y = y)) +
geom_point() +
xlim(x.min, x.max) +
ylim(y.min, y.max) +
coord_equal() +
theme(aspect.ratio = 1)
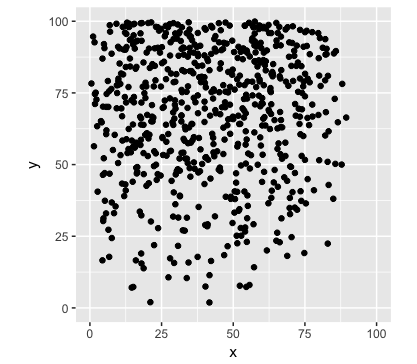
fit3 <- stan("ipp.stan",
data = list(NX = nrow(df3),
NP = nrow(df3),
NU = nrow(w),
X = as.matrix(df3),
P = as.matrix(df3),
U = as.matrix(w),
E = lx * ly,
sigma = 2),
iter = 2000, warmup = 1000, thin = 1)
print(fit3)
結果です。a1は14くらいと推定されました。
Inference for Stan model: ipp.
4 chains, each with iter=2000; warmup=1000; thin=1;
post-warmup draws per chain=1000, total post-warmup draws=4000.
mean se_mean sd 2.5% 25% 50% 75% 97.5% n_eff
a0 -4.04 0.00 0.08 -4.19 -4.09 -4.04 -3.98 -3.88 1130
a1 14.14 0.02 0.56 13.02 13.75 14.13 14.52 15.22 1141
lp__ -2200.68 0.02 0.93 -2203.29 -2201.07 -2200.39 -2200.02 -2199.77 1521
Rhat
a0 1
a1 1
lp__ 1





コメント 0