MCMC再訪(2): ロジスティック回帰 [統計]
(1)につづき、今回はロジスティック回帰をやってみる。
ある生物の集団があったとする。K = 10個体ずつに、X (X1 = 0, X2 = 1, X3 = 2,..., X11 = 10)単位だけある薬品を与えたところ、それぞれについて10個体中のYi個体が死亡したとする。このとき、XとYとの関係をモデル化し、パラメータを推定する。
以下のようなコード
library(R2WinBUGS)
R2WinBUGSパッケージを使用する。
## data K <- 10 X <- c(0, 1, 2, 3, 4, 5, 6, 7, 8, 9, 10) Y <- c(1, 2, 2, 6, 4, 5, 8, 9, 9, 9, 10) N <- length(X)
データを用意。
model <- function() {
for (i in 1:N) {
Y[i] ~ dbin(p[i], K);
logit(p[i]) <- beta + beta.x * X[i];
}
# priors
beta ~ dnorm(1.0E-6, 1.0E-6);
beta.x ~ dnorm(1.0E-6, 1.0E-6);
}
write.model(model, "sample2.bug")
モデル。Y[i]は、試行数K、確率p[i]の二項分布に従うとする。p[i]とX[i]との関係が次の行。betaおよびbeta.xはパラメータで、事前分布は無情報とする。
## Settings
platform <- .Platform$OS.type
if (platform == "unix") {
useWINE = TRUE
## check Darwine
darwine.bin <- "/Applications/Darwine/Wine.bundle/Contents/bin"
if (file.exists(darwine.bin)) {
wine <- paste(darwine.bin, "wine", sep = "/")
winepath <- paste(darwine.bin, "winepath", sep = "/")
} else {
## use `which'
wine <- system("which wine", intern = TRUE)
winepath <- system("which winepath", intern = TRUE)
if (wine == ""|| winepath == "") {
stop("Wine not found.")
}
}
bugs.dir <- paste(Sys.getenv("HOME"),
".wine/drive_c/Program Files/WinBUGS14",
sep = "/")
if (!file.exists(bugs.dir)) {
stop("bugs directory not found.")
}
} else if (platform == "windows") {
## Windows
useWINE = FALSE
bugs.dir <- "C:/Program Files/WinBUGS14"
if (!file.exists(bugs.dir)) {
stop("bugs directory not found.")
}
wine <- NULL
winepath <- NULL
}
実行環境に応じた設定をおこなう。
## number of chains n.chains <- 3 ## initial values init1 <- list(beta = -10, beta.x = 0) init2 <- list(beta = -5, beta.x = 2) init3 <- list(beta = 0, beta.x = 4)
chainの数と、初期値を用意する。
## MCMC
post.samp <- bugs(data = list(X = X, Y = Y, N = N, K = K),
inits = list(init1, init2, init3),
parameters.to.save = c("beta", "beta.x"),
model = "sample2.bug",
n.chains = n.chains,
n.iter = 21000,
n.burnin = 1000,
n.thin = 10,
debug = FALSE,
bugs.directory = bugs.dir,
working.directory = getwd(),
clearWD = TRUE,
useWINE = useWINE,
newWINE = TRUE,
WINE = wine,
WINEPATH = winepath)
WinBUGSの実行
print(post.samp, digits = 3)
結果の表示。以下の結果が表示される。
Inference for Bugs model at "sample2.bug", fit using WinBUGS,
3 chains, each with 21000 iterations (first 1000 discarded), n.thin = 10
n.sims = 6000 iterations saved
mean sd 2.5% 25% 50% 75% 97.5% Rhat n.eff
beta -2.161 0.492 -3.164 -2.484 -2.144 -1.823 -1.246 1.001 3000
beta.x 0.556 0.101 0.372 0.486 0.552 0.621 0.763 1.001 6000
deviance 30.078 2.024 28.140 28.670 29.460 30.880 35.481 1.001 6000
For each parameter, n.eff is a crude measure of effective sample size,
and Rhat is the potential scale reduction factor (at convergence, Rhat=1).
DIC info (using the rule, pD = Dbar-Dhat)
pD = 2.0 and DIC = 32.0
DIC is an estimate of expected predictive error (lower deviance is better).
## mcmc object
post.mcmc <- mcmc.list(lapply(1:(post.samp$n.chain),
function(chain)
as.mcmc(post.samp$sims.array[,chain,])))
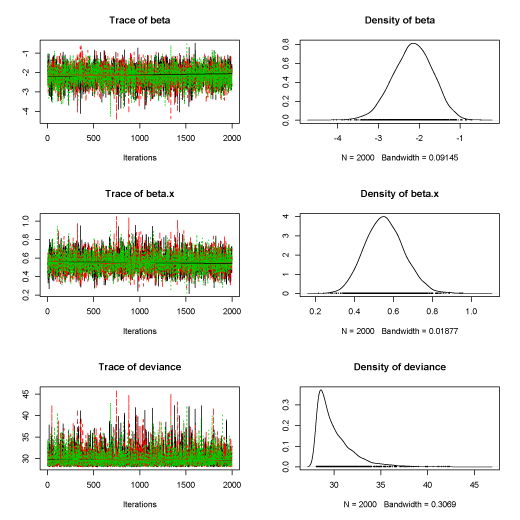
plot(post.mcmc)
軌跡と密度を表示する。
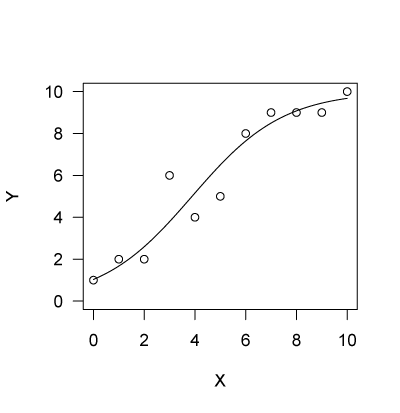
beta <- post.samp$mean$beta beta.x <- post.samp$mean$beta.x x <- seq(0, 10, len = 100) logit.p <- beta + beta.x * x exp.Y <- K * exp(logit.p) / (1 + exp(logit.p)) plot(X, Y, type = "p", ylim = c(0, 10), las = 1) lines(x, exp.Y)
データと、MCMCから求められた期待とを重ねてプロットする。





やはりそちらの世界ではSPSSを使ってはいけないものですか。
by 春分 (2009-09-05 15:54)
別にSPSSを使ってはいけないことはないですし、実際使っている人もいますが、まあこのあたりは個人的な嗜好というか、でもRは無料だし、とか。
by hiroki (2009-09-05 19:13)
なるほど嗜好ですね。ダシはダシノモトとかには頼らず、鰹節からとると。
by 春分 (2009-09-05 20:33)
でも実際のダシは このごろは白だしを使っていたり。
by hiroki (2009-09-06 05:44)