hSDM.ZIP.iCARでうまくいかなかった例 [統計]
hSDMでIntrinsic CARをつかたZIPモデルをつかってみましたが、うまくいかなかったという例です。
データは、以前もつかったアラカシのデータです。コードは以下のとおり。
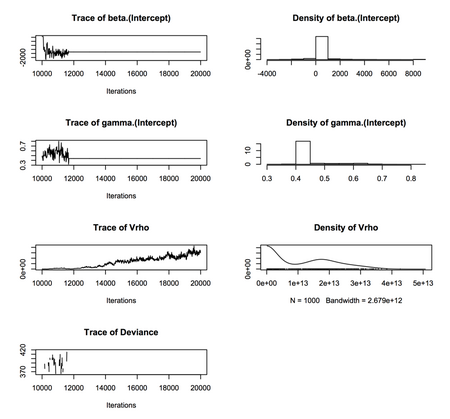
library(hSDM) library(coda) ## Data ## http://cse.ffpri.affrc.go.jp/hiroki/stat/Qglauca.csv qg <- read.csv("Qglauca.csv") ## Adjacent cells adj <- c(2, 11, # 1 c(sapply(2:9, function(i) i + c(-1, 1, 10))), # 2--9 9, 20, # 10 c(sapply(seq(0, 170, 10), function(j) j + c(1, 12, 21, c(sapply(2:9, function(i) i + c(0, 9, 11, 20))), 10, 19, 30))), # 10--190 181, 192, # 191 c(sapply(2:9, function(i) i + c(180, 189, 191))), # 192--199 190, 199) # 200 num.adj <- c(2, rep(3, 8), 2, rep(c(3, rep(4, 8), 3), 18), 2, rep(3, 8), 2) qg$cell <- 1:nrow(qg) pred <- data.frame(cell = qg$cell, X = qg$X, Y = qg$Y) fit.zip <- hSDM.ZIP.iCAR(counts = qg$N, suitability = ~1, abundance = ~1, spatial.entity = qg$cell, data = qg, n.neighbors = num.adj, neighbors = adj, burnin = 10000, mcmc = 10000, thin = 10, beta.start = 0, gamma.start = 0, Vrho.start = 10) plot(fit.zip$mcmc)
しかし軌跡をみるとVrhoがどんどん発散していっているようです。うーむ。





コメント 0