R: RStanをためす [統計]
あたらしいBayes推定ソフトウェアであるStan 1.0.0と、そのRインターフェスのRStan 1.0.0が発表されている(Revolutions: RStan: Fast, multilevel Bayesian modeling in R)。
Stan → C++ → ネイティブバイナリ
と、コンパイルして高速に計算できということだ。
さっそくためしてみる。
library(rstan)
x <- rpois(30, 4)
model <- '
data {
int<lower=0> n; // number of data
int<lower=0> x[n]; // data
}
parameters {
real<lower=0> lambda; // mean
}
model {
for (i in 1:n) {
x[i] ~ poisson(lambda);
}
lambda ~ gamma(0.001, 0.001);
}
'
data <- list(n = length(x), x = x)
fit <- stan(model_code = model, data = data,
warmup = 500, iter = 1500, chains = 4)
結果
> fit >- stan(model_code = model, data = data,
+ warmup = 500, iter = 1500, chains = 4)
TRANSLATING MODEL 'anon_model' FROM Stan CODE TO C++ CODE NOW.
COMPILING THE C++ CODE FOR MODEL 'anon_model' NOW.
SAMPLING FOR MODEL 'anon_model' NOW (CHAIN 1).
Iteration: 1500 / 1500 [100%] (Sampling)
SAMPLING FOR MODEL 'anon_model' NOW (CHAIN 2).
Iteration: 1500 / 1500 [100%] (Sampling)
SAMPLING FOR MODEL 'anon_model' NOW (CHAIN 3).
Iteration: 1500 / 1500 [100%] (Sampling)
SAMPLING FOR MODEL 'anon_model' NOW (CHAIN 4).
Iteration: 1500 / 1500 [100%] (Sampling)
>
> print(fit)
Inference for Stan model: anon_model.
4 chains: each with iter=1500; warmup=500; thin=1; 1500 iterations saved.
mean se_mean sd 2.5% 25% 50% 75% 97.5% n_eff Rhat
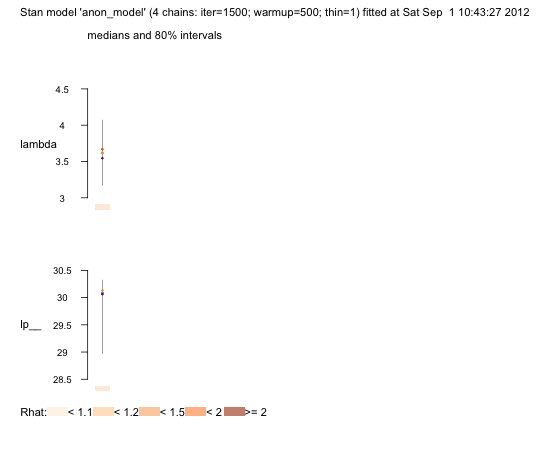
lambda 3.6 0 0.4 3.0 3.4 3.6 3.9 4.3 824 1
lp__ 29.8 0 0.7 27.8 29.6 30.1 30.3 30.3 745 1
Sample were drawn using NUTS2 at Sat Sep 1 10:43:27 2012.
For each parameter, n_eff is a crude measure of effective sample size,
and Rhat is the potential scale reduction factor on split chains (at
convergence, Rhat=1).
> plot(fit)
traceplot(fit)
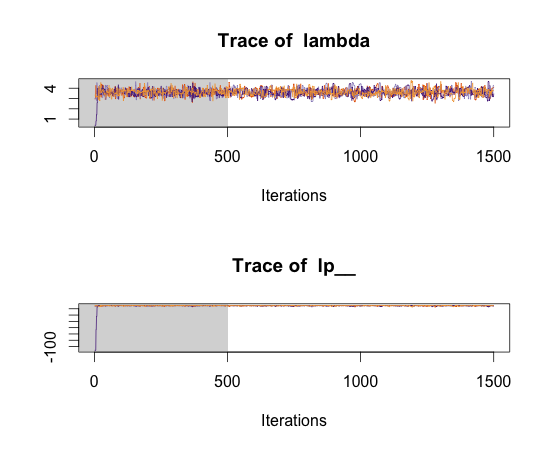
lp__は、"the log probability function value at the sample"だとマニュアルに説明がある。
このくらいのモデルだとコンパイルの方に時間がかかってしまうが、複雑なモデルなら効果的であろう。





コメント 0